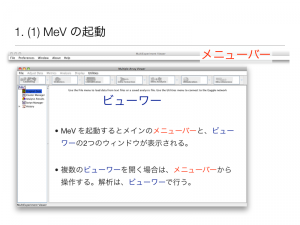
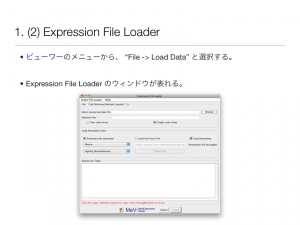
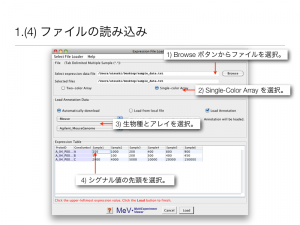
ファイル読み込み後の操作方法を説明します。
- ラベル変更方法
- グループ名の設定
- シグナル値の log2 変換
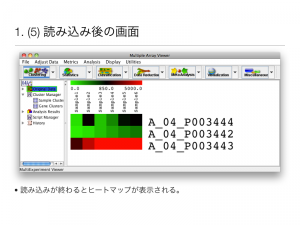
(6) ラベルの表示変更
各プローブにつけられたラベルは、メニューから、”Display -> Gene/Row Labels -> Label by GeneSymbol” などとして変更可能。
*読み込み時に “Automaticaly download” と “Load Annotation” にチェックを入れて、生物種とアレイの製品名を選択すれば、自動的にアノテーションがダウンロードされ、ラベルとして使用できるようになります。すべての製品に対応しているわけではありませんし、ダウンロードされるアノテーションが最新のデータとは限りませんので、表示したいアノテーションは、あらかじめ準備されることを推奨します。
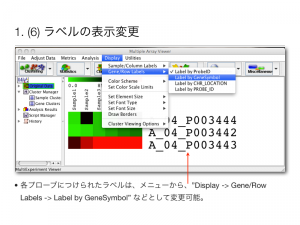
(7) サンプルのグループ名の設定
- Sample Cluster を選択。
- サンプルを複数選択。 (連続した領域は、シフトを押しながら複数選択できます。連続していない領域を複数選択する場合は、 Windows は Ctrl キー、 Mac はコマンドキーを押しながら選択します。)
- Store Rows as Cluster を選択。
- グループ名を入力。
*検定などを行う際は、ここでグループを設定しておくと便利です。ラベルの色も選択して、変更できます。
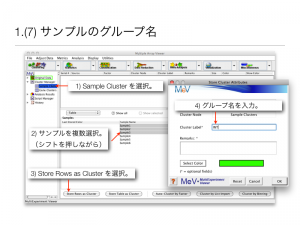
設定例: WT と KO の2グループを設定
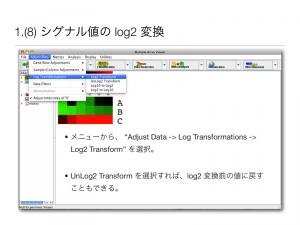
(8) シグナル値の log2 変換
- メニューから、 “Adjust Data -> Log Transformations -> Log2 Transform” を選択。
- UnLog2 Transform を選択すれば、log2 変換前の値に戻すこともできる。