GOを使うと何でも解析できるというわけではありません。GOには、その構造上、得意な点と不得意な点があります。
GOの得意な点
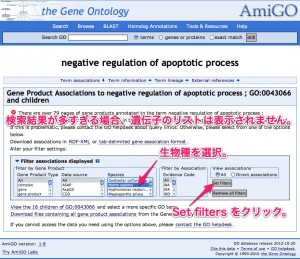
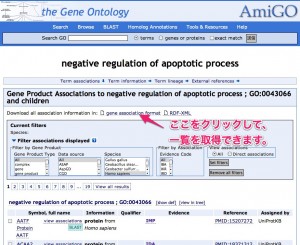
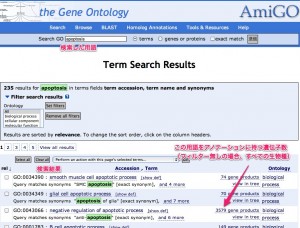
マイクロアレイ解析の結果から、特定の用語(機能、キーワード)を持つ遺伝子だけを取り出せます。マイクロアレイ解析の結果を表示したエクセルのGOの列を検索すればよいです。または、AmiGO で、GOの特定の用語を持つ遺伝子のリストをあらかじめ取得しておき、遺伝子名を検索する方法もあります。(探したい遺伝子が1個か2個なら、よいのですが、大量に検索するときは、データを一度データベースに登録して、SQL言語を利用するなど、情報処理の技術を使うことをお勧めします。人的ミスを防げますし、時間がかかりません。ご相談ください。)
GOの不得意な点
当然ながら、GOに登録されていない用語(機能、キーワード)を扱うことができません。例えば、 “apoptosis” ではなく、 “apoptotic process” でなければなりません。”response to tumor necrosis factor” (GO:0034612) はありますが、 “tumorigenesis” はありません。”oncogenesis” という用語も現在は使われていません。流行の stemness genes はありませんが、 “stem cell differentiation” (GO:0048863) はあります。
よく使われる用語であっても、意外と登録されていなかったりします。(登録されていない原因はいろいろです。言い換えができたり、GOの思想と合わないなど。)この場合は、単語を区切るなり、別のいい方を考えたり、もっと細かいプロセスに分解して考える必要があります。
“tumorigenesis” の例でいえば、GOの用語中に “tumor” を含むものすべてという選び方をする必要があります。また、転移 (metastasis) に関連する遺伝子を選びたいとしても、 GO に “metastasis” はありませんので、GO:0051726 : regulation of cell cycle と GO:0007155 : cell adhesion と GO:0042379 : chemokine receptor binding というように複数のプロセスに分けて考え、それらをGOに持つものすべてを対象として選択することになります。